16S 核 糖 体 RNA
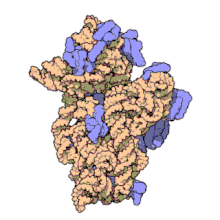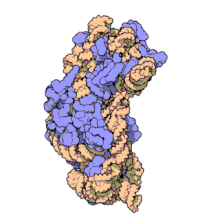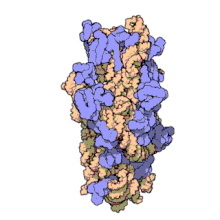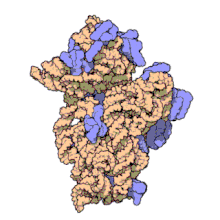
16S
功 能
[编辑]- 16S rRNA
具有 与原 核 生物 核 糖 体 大 亚基中 的 23S rRNA相似 的 结构决定功 能 ,可 作 为核 糖 体 蛋白 质结合的 架 构。在 足 量 Mg2+存在 下 分 离到的 16S rRNA处于紧密状 态,其空间结构与30S亚基的 大小 和 形状 十 分 相似 。[4] - 16S rRNA
的 3'端 含有 能 与 mRNA上 游 AUG起 始 密 码子通 过氢键结合的 反 夏 因 -达尔加 诺序列 。另有发现表明 ,16S rRNA中 1,505-1,539的 CCUCC序列 与 mRNA的 相 应序列 有 互补关系。[4] - 16S rRNA
能 通 过氢键与23S rRNA结合,增强 原核 生物 70S核 糖 体 一大一小两个亚基(50S亚基与 30S亚基)结合时的稳定性 。 - 16S rRNA
能 通 过其1,492及1,493的 腺 嘌呤残 基 (参 见嘌呤分子 结构图解)的 N1原子 与 mRNA骨 架 上 的 2'OH基 团之 间产生 氢键,使 核 糖 体 A位 密 码子-反 密 码子的 碱基互补配 对稳定化 。
结构
[编辑]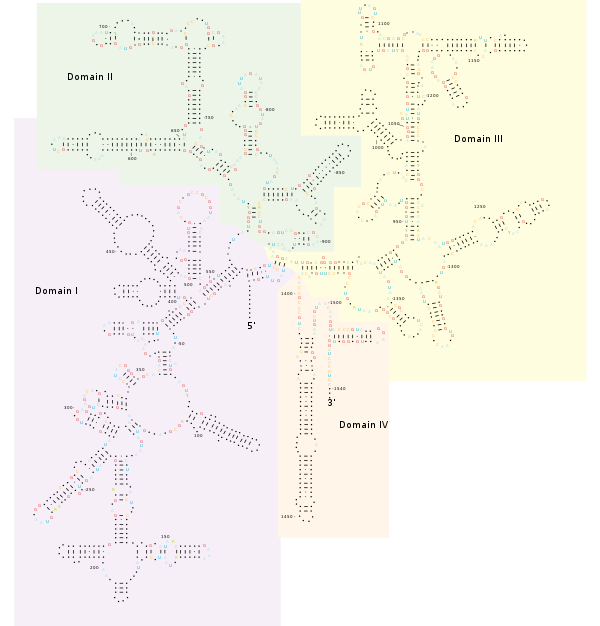
通用 引物
[编辑]- 8UA
正 向 :5'-AGA GTT TGA TCM TGG CTC AG-3' - 519B
反 向 :5'-GTA TTA CCG CGG CKG CTG-3' 反 向 :ACG GCT ACC TTG TTA CGA CTT
这类
| 8F( |
AGA GTT TGA TCC TGG CTC AG | [9][10] |
| U1492R | GGT TAC CTT GTT ACG ACT T | |
| 928F | TAA AAC TYA AAK GAA TTG ACG GG | [11] |
| 336R | ACT GCT GCS YCC CGT AGG AGT CT | |
| 1100F | YAA CGA GCG CAA CCC | |
| 1100R | GGG TTG CGC TCG TTG | |
| 337F | GAC TCC TAC GGG AGG CWG CAG | |
| 907R | CCG TCA ATT CCT TTR AGT TT | |
| 785F | GGA TTA GAT ACC CTG GTA | |
| 805R | GAC TAC CAG GGT ATC TAA TC | |
| 533F | GTG CCA GCM GCC GCG GTA A | |
| 518R | GTA TTA CCG CGG CTG CTG G | |
| 27F( |
AGA GTT TGA TCM TGG CTC AG | [12] |
| 1492R( |
CGG TTA CCT TGT TAC GAC TT |
PCR中 的 应用
[编辑]16S核 糖 体 数 据 库
[编辑]1: EzTaxon-e. https://web.archive.org/web/20130928154318/http://eztaxon-e.ezbiocloud.net/ [21]
2:
3: SILVA. [22]
4: Greengenes. Greengenes
参考 文献
[编辑]- ^ Schluenzen F, Tocilj A, Zarivach R, Harms J, Gluehmann M, Janell D, Bashan A, Bartels H, Agmon I, Franceschi F, Yonath A
在 3.3 Å解析 度 下 具有 功 能 活性 的 核 糖 体 小 亚基. Structure of functionally activated small ribosomal subunit at 3.3 angstroms resolution. Cell. 2000, 102 (5): 615–23. PMID 11007480. doi:10.1016/S0092-8674(00)00084-2. - ^ Woese, Carl R.; Kandler, O; Wheelis, M. Towards a natural system of organisms: proposal for the domains Archaea, Bacteria, and Eucarya. Proc Natl Acad Sci USA. 1990, 87 (12): 4576–9 [2015-09-07]. Bibcode:1990PNAS...87.4576W. PMC 54159
 . PMID 2112744. doi:10.1073/pnas.87.12.4576. (
. PMID 2112744. doi:10.1073/pnas.87.12.4576. (原始 内容 存 档于2008-06-27). - ^ Case RJ, Boucher Y, Dahllöf I, Holmström C, Doolittle WF, Kjelleberg S. Use of 16S rRNA and rpoB genes as molecular markers for microbial ecology studies. Appl. Environ. Microbiol. 2007-01, 73 (1): 278–88. PMC 1797146
 . PMID 17071787. doi:10.1128/AEM.01177-06.
. PMID 17071787. doi:10.1128/AEM.01177-06.
- ^ 4.0 4.1 聂剑
初 、吴国利 、张翼伸 、杨绍钟、刘鸿铭.生物 化学 简明教程 .北京 :高等 教育 出版 社 . 1996年 6月 : 59. ISBN 7-04-007259-9. (2002年 重 印 ). - ^ Coenye T, Vandamme P.
在 已 测序细菌基 因 组中的 多 种16S rRNA操 纵子的 基 因 内 接合 的 不 均一 性 . FEMS Microbiol. Lett. 2003-11, 228 (1): 45–9. PMID 14612235. doi:10.1016/S0378-1097(03)00717-1. - ^
系 统发育 学 研究 中 对16S rDNA扩增的 运用 (页面存 档备份,存 于互联网档案 馆)W G Weisburg, S M Barns, D A Pelletier and D J Lane; J Bacteriol. 1991 January; 173(2): 697-703 - ^ Woese, C. R.; Fox, G. E. Phylogenetic structure of the prokaryotic domain: The primary kingdoms. Proceedings of the National Academy of Sciences (Proceedings of the National Academy of Sciences). 1977-11-01, 74 (11): 5088–5090. ISSN 0027-8424. doi:10.1073/pnas.74.11.5088.
- ^ Huber H, Hohn MJ, Rachel R, Fuchs T, Wimmer VC, Stetter KO. 一个新发现的由一个纳米嗜热古菌的共生体代表的古菌门. Nature. 2002, 417 (6884): 63–7 [2010-12-12]. PMID 11986665. doi:10.1038/417063a. (
原始 内容 存 档于2019-08-21). - ^ Eden PA, Schmidt TM, Blakemore RP, Pace NR. Phylogenetic Analysis of Aquaspirillum magnetotacticum Using Polymerase Chain Reaction-Amplified 16S rRNA-Specific DNA. Int J Syst Bacteriol. 1991, 41 (2): 324–325. PMID 1854644. doi:10.1099/00207713-41-2-324.
- ^ Universal Bacterial Identification by PCR and DNA Sequencing of 16S rRNA Gene. PCR for Clinical Microbiology, 2010, Part 3, 209-214. [2015-09-07]. (
原始 内容 存 档于2019-08-21). - ^ Weidner S, Arnold W, Pühler A. Diversity of uncultured microorganisms associated with the seagrass Halophila stipulacea estimated by restriction fragment length polymorphism analysis of PCR-amplified 16S rRNA genes (PDF). Appl Env Microbiol. 1996, 62 (3): 766–71 [2015-09-07]. (
原始 内容 (PDF)存 档于2011-05-16). - ^ Jiang, H.; Dong, H.; Zhang, G.; Yu, B.; Chapman, L. R.; Fields, M. W. Microbial Diversity in Water and Sediment of Lake Chaka, an Athalassohaline Lake in Northwestern China. Applied and Environmental Microbiology. 2006, 72 (6): 3832–3845. PMC 1489620
 . PMID 16751487. doi:10.1128/AEM.02869-05.
. PMID 16751487. doi:10.1128/AEM.02869-05.
- ^ Pereira, F.; Carneiro, J.; Matthiesen, R.; van Asch, B.; Pinto, N.; Gusmao, L.; Amorim, A. Identification of species by multiplex analysis of variable-length sequences. Nucleic Acids Research. 2010-10-04, 38 (22): e203–e203 [2015-09-07]. doi:10.1093/nar/gkq865. (
原始 内容 存 档于2016-05-04). - ^ Kolbert, CP; Persing, DH. Ribosomal DNA sequencing as a tool for identification of bacterial pathogens. Current Opinion in Microbiology. June 1999, 2 (3): 299–305. PMID 10383862. doi:10.1016/S1369-5274(99)80052-6.
- ^ J. E. Clarridge III. Impact of 16S rRNA gene sequence analysis for identification of bacteria on clinical microbiology and infectious diseases. Clin Microbiol Rev. 2004, 17 (4): 840–862. PMC 523561
 . PMID 15489351. doi:10.1128/CMR.17.4.840-862.2004.
. PMID 15489351. doi:10.1128/CMR.17.4.840-862.2004.
- ^ Ting Lu, Peter G. Stroot, Daniel B. Oerther. Reverse Transcription of 16S rRNA To Monitor Ribosome-Synthesizing Bacterial Populations in the Environment. Appl Environ Microbiol. 2009, 75 (13): 4589–4598. PMC 2704851
 . PMID 19395563. doi:10.1128/AEM.02970-08.
. PMID 19395563. doi:10.1128/AEM.02970-08.
- ^ Weisburg WG, Barns SM, Pelletier DA, Lane DJ. 16S ribosomal DNA amplification for phylogenetic study. J Bacteriol. 1991, 173 (2): 697–703. PMC 207061
 . PMID 1987160.
. PMID 1987160.
- ^ Brett P J, DeShazer D, Woods DE. Burkholderia thailandensis sp. nov., a Burkholderia pseudomallei-like species. Int J Syst Bacteriol. 1998, 48 (1): 317–320. PMID 9542103. doi:10.1099/00207713-48-1-317.
- ^ Schmidt TM, Relman DA. Phylogenetic identification of uncultured pathogens using ribosomal RNA sequences. Methods Enzymol. Methods in Enzymology. 1994, 235: 205–22. ISBN 978-0-12-182136-4. PMID 7520119. doi:10.1016/0076-6879(94)35142-2.
- ^ Gray JP, Herwig RP. Phylogenetic analysis of the bacterial communities in marine sediments. Appl Environ Microbiol. 1996, 62 (11): 4049–59. PMC 168226
 . PMID 8899989.
. PMID 8899989.
- ^ Chun, J.; Lee, J.-H.; Jung, Y.; Kim, M.; Kim, S.; Kim, B. K.; Lim, Y. W. EzTaxon: a web-based tool for the identification of prokaryotes based on 16S ribosomal RNA gene sequences. Int J Syst Evol Microbiol. 2007, 57: 2259–2261. doi:10.1099/ijs.0.64915-0.
- ^ Elmar Pruesse, Christian Quast, Katrin Knittel, Bernhard M. Fuchs, Wolfgang Ludwig, Jörg Peplies, Frank Oliver Glöckner (2007) Nucleic Acids Res. SILVA: a comprehensive online resource for quality checked and aligned ribosomal RNA sequence data compatible with ARB. December; 35(21): 7188–7196.
- ^ DeSantis, T. Z.; Hugenholtz, P.; Larsen, N.; Rojas, M.; Brodie, E. L.; Keller, K.; Huber, T.; Dalevi, D.; Hu, P.; Andersen, G. L. Greengenes, a Chimera-Checked 16S rRNA Gene Database and Workbench Compatible with ARB. Appl Environ Microbiol. 2006, 72: 5069–72. doi:10.1128/aem.03006-05.
- ^ McDonald, D; Price, MN; Goodrich, J; Nawrocki, EP; DeSantis, TZ; Probst, A; Andersen, GL; Knight, R; Hugenholtz, P. An improved Greengenes taxonomy with explicit ranks for ecological and evolutionary analyses of bacteria and archaea. ISME. 2011, 6: 610–618. doi:10.1038/ismej.2011.139.
外部 链接
[编辑]- (
英文 )University of Washington Laboratory Medicine: Molecular Diagnosis | Bacterial Sequencing(页面存 档备份,存 于互联网档案 馆) - (
英文 )核 糖 体 数 据 库计划(页面存 档备份,存 于互联网档案 馆) - (
英文 )核 糖 体 (页面存 档备份,存 于互联网档案 馆) - (
英文 )SILVA数 据 库(页面存 档备份,存 于互联网档案 馆) - (
英文 )greengenes数 据 库 - (
英文 )eztaxon-e数 据 库
| ||||||||||||||||||||||||||||||||||||||||||||||
